Communications Biology | 徐佩佩课题组利用全基因组核糖体图谱技术揭示植物根系响应模拟微重力的翻译调控机制
随着人类深空探测事业的持续推进,太空环境下的作物种植已成为保障长期载人航天任务顺利开展的核心关键技术。微重力作为太空植物栽培面临的首要环境胁迫,其对植物生长发育的调控机制一直是科学界的研究热点。然而,以往相关研究多聚焦于基因转录水平的响应规律,对蛋白质合成关键环节——翻译水平的调控机制却知之甚少,这一认知空白极大地限制了对植物适应空间环境分子机制的全面理解。

针对这一研究缺口,我院徐佩佩课题组在国际期刊《Communications Biology》发表题为“Genome-wide ribosome profiling reveals a dynamic translational landscape in Arabidopsis seedling roots under simulated microgravity”的研究论文,通过核糖体图谱技术(Ribo-seq)与转录组测序(RNA-seq)的整合分析,首次系统绘制了拟南芥幼苗根系响应模拟微重力的全基因组翻译调控图谱(图1),填补了该领域翻译调控研究的空白。
研究团队采用地面3D回转系统模拟微重力条件,以拟南芥幼苗为研究对象,运用核糖体图谱分析技术(Ribo-seq)——该技术可通过捕获核糖体保护的mRNA片段,精确定量基因翻译活性,实现全基因组水平翻译动态的实时监测——对模拟微重力条件下的拟南芥进行系统检测,并将其与传统转录组测序(RNA-seq)数据进行深度比较分析。全基因组层面的对比结果显示,仅有不到三分之一的微重力响应基因在转录与翻译水平同步发生表达变化(图2)。这一关键发现清晰表明,模拟微重力可在植物体内诱导独立的转录响应与翻译响应,植物并非仅依赖传统的基因转录调控来适应微重力环境,而是启动了一套独立于转录过程的特异性翻译调控机制,为植物适应空间环境提供了全新的分子调控路径。

图 1. 模拟微重力条件下拟南芥根系的转录与翻译响应
(a) 对 6 日龄 Col-0 拟南芥幼苗根系进行核糖体图谱分析(Ribo-seq)和转录组测序(RNA-seq),样本分为正常生长条件组和模拟微重力处理组。 (b) 核糖体图谱分析(Ribo-seq)和转录组测序(RNA-seq)数据的表达丰度分布。横坐标表示 log10 FPKM 值,虚线清晰区分对照组(CK)和 3D 回转处理组(Col-3D)的转录与翻译丰度。
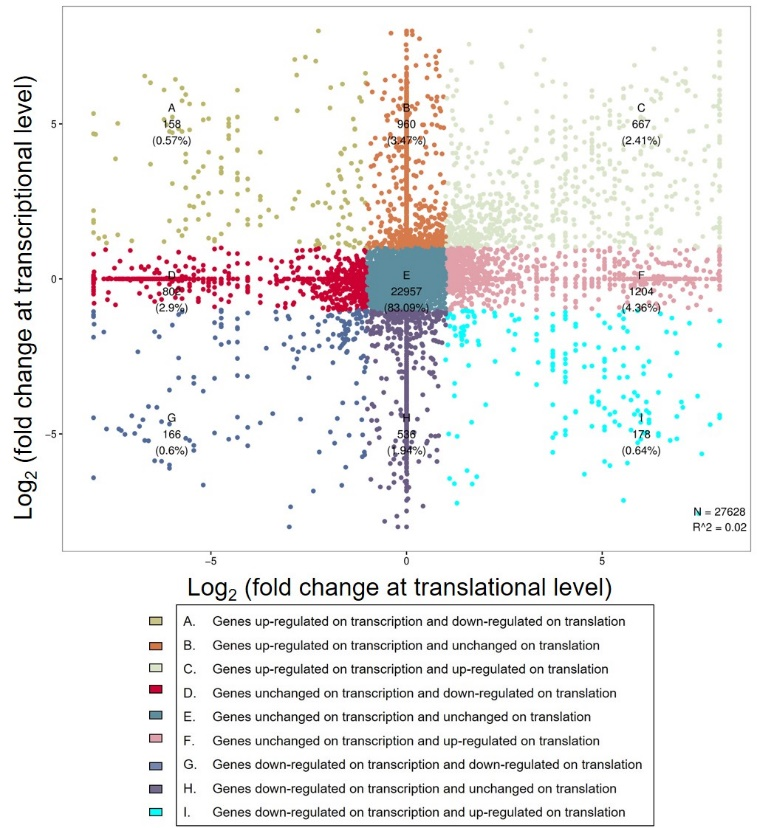
图2. 模拟微重力条件下转录水平和翻译水平FPKM的倍数变化
研究鉴定出1081个在模拟微重力条件下翻译效率发生显著改变的基因,这些基因广泛参与细胞壁重塑、氧化应激响应、激素信号传导等植物适应逆境的关键生理过程,为解析植物微重力适应的分子路径提供了重要靶点。通过对这些差异基因的序列特征分析,研究团队明确了GC含量、编码序列(CDS)长度等特定序列特征是影响基因翻译效率的关键因素(图2);同时发现,基因启动子区域中上游开放阅读框(uORFs)的丰度的差异,也可能通过调控核糖体的起始或扫描过程,对下游主要开放阅读框的翻译效率产生重要 调控作用,这与当前uORFs参与翻译调控的研究结论相一致。
本研究由中山大学农业与生物技术学院与中科院分子植物科学卓越创新中心联合合作完成,论文第一完成单位为中山大学农业与生物技术学院。博士后张婷、博士后张力爽及分子植物卓越中心博士生杨一琳为论文共同第一作者;中山大学徐佩佩副教授、中科院分子植物卓越中心蔡伟明研究员和郑慧琼研究员为共同通讯作者。
该研究得到国家自然科学基金、中国载人航天工程、上海市自然科学基金及中国科学院战略性先导科技专项等多个项目的资助。为后续培育适应空间环境的作物新品种、推动太空农业发展提供了重要的理论依据与潜在靶点。
初稿:张婷 初审:徐佩佩 审核:辛国荣 终审:杨德胜



